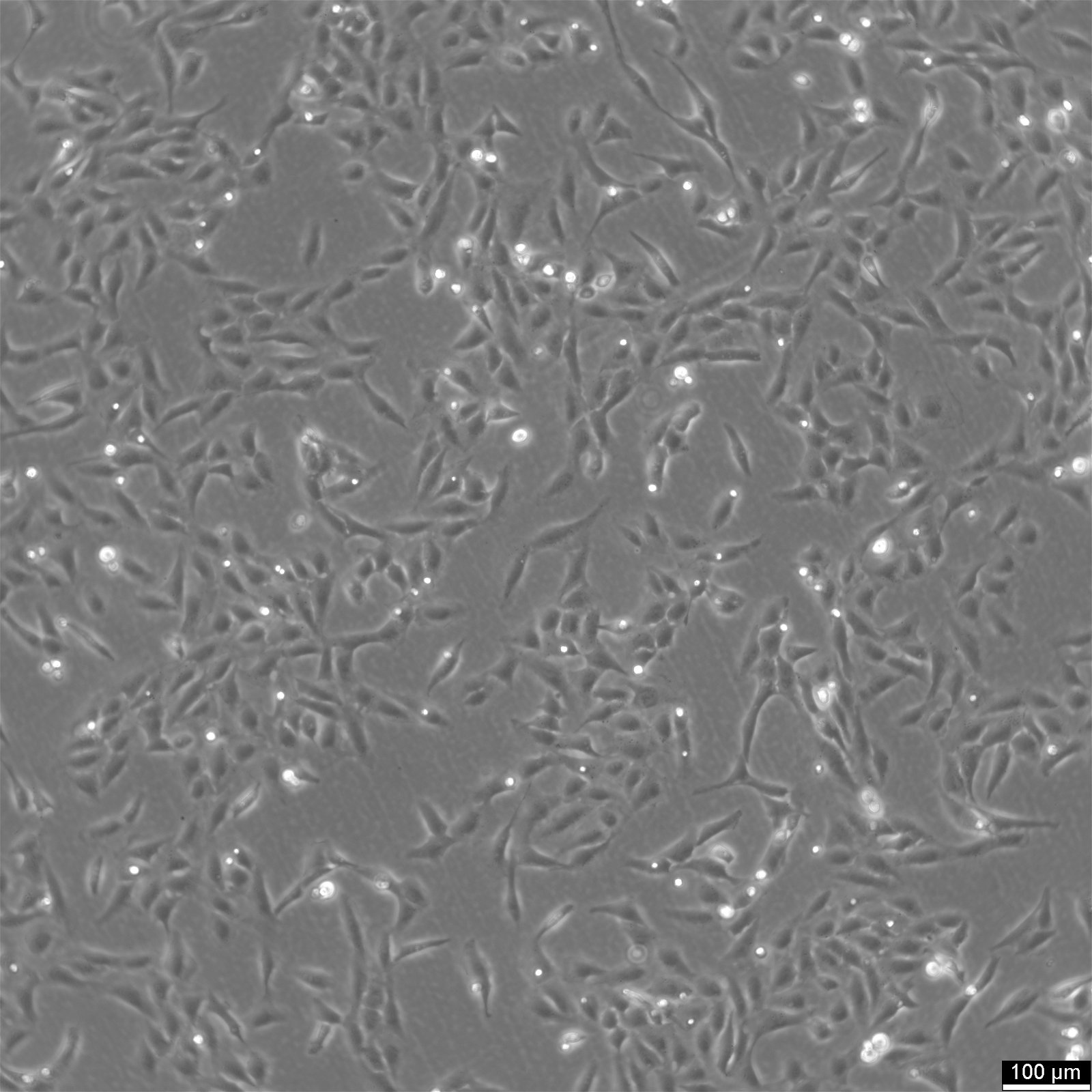
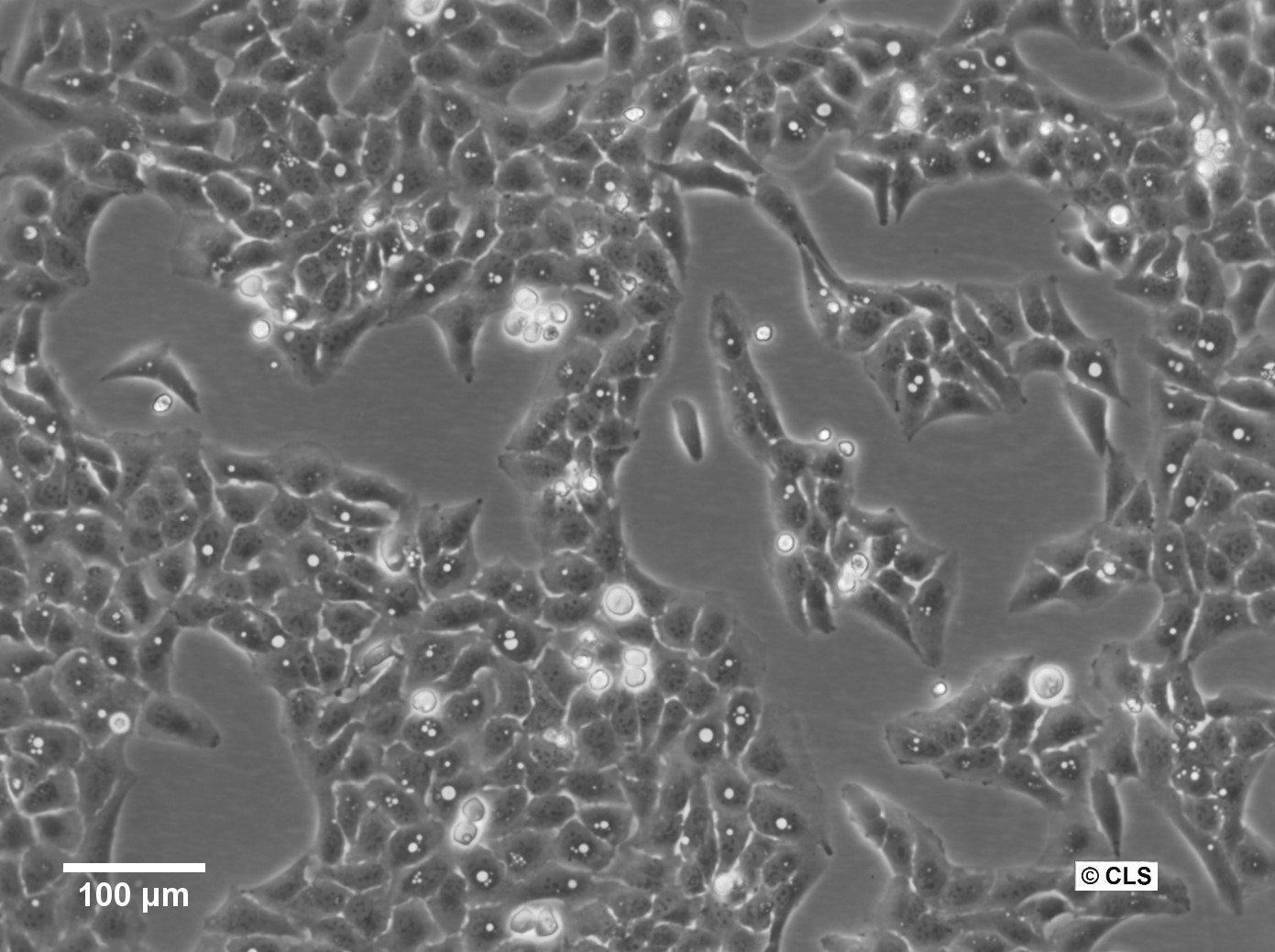
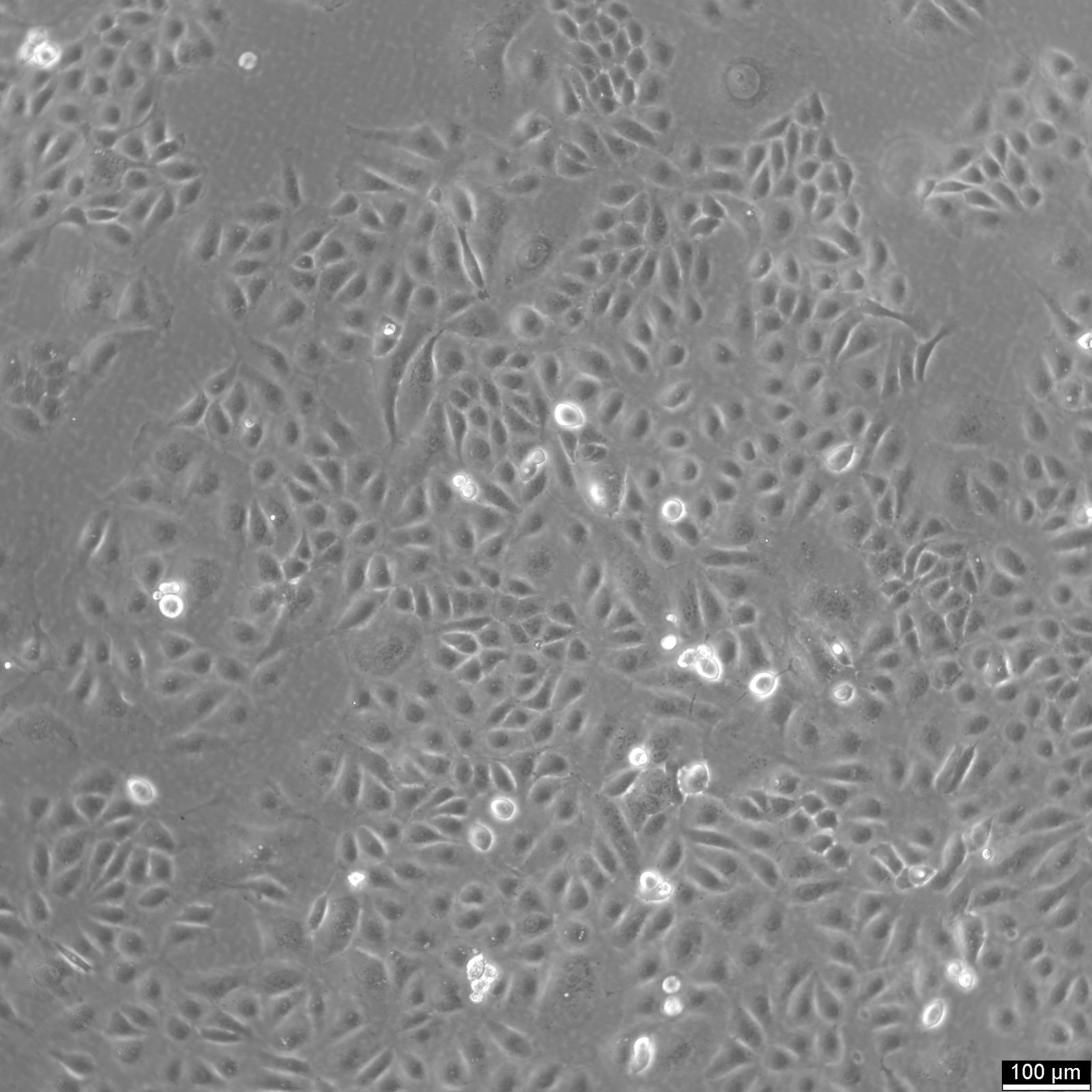
Células U2OS-CRISPR-SNAPf-SEH1
800,00 €*
Los productos se envían congelados en hielo seco en criotubos. Cada criotubo contiene normalmente 3 × 10 6 células para líneas adherentes o 5 × 106 células para líneas en suspensión (consulte el certificado de análisis del lote para obtener más detalles).
Información general
| Descripción | U2OS-CRISPR-SNAPf-SEH1 es una línea celular de osteosarcoma humano editada genómicamente derivada de células U2OS en la que se ha modificado el gen SEH1L (SEH1) endógeno mediante la tecnología CRISPR/Cas9 para codificar una etiqueta SNAPf en marco. SEH1 es un componente del complejo Y (también conocido como complejo NUP107-160), un módulo estructural central del complejo de poros nucleares (NPC) que contribuye al ensamblaje y la estabilidad del andamio de los poros. Al insertar la secuencia codificante SNAPf en el locus endógeno, la proteína SEH1 etiquetada se expresa bajo control regulador nativo, lo que preserva los niveles de expresión fisiológicos y minimiza las perturbaciones en la composición de los poros nucleares. La etiqueta SNAPf es una variante modificada genéticamente y de rápida reacción de la etiqueta SNAP que se une covalentemente a sustratos conjugados con bencilguanina, lo que permite un marcaje fluorescente selectivo y estable en células vivas o fijadas. En las células U2OS-CRISPR-SNAPf-SEH1, la proteína de fusión se localiza en la envoltura nuclear con un patrón punteado característico de la distribución del NPC. Dado que el marcaje se produce a niveles de proteína endógena, este sistema es muy adecuado para la microscopía de fluorescencia cuantitativa, la obtención de imágenes de superresolución y los análisis de seguimiento de partículas individuales destinados a diseccionar la organización y la estequiometría de los NPC. La morfología plana y los núcleos grandes de las células U2OS facilitan aún más la visualización de alta resolución de las estructuras de la envoltura nuclear. SEH1 participa en la biogénesis de los NPC y también se ha implicado en procesos asociados al cinetocoro durante la mitosis. En consecuencia, esta línea celular proporciona una plataforma sólida para investigar el ensamblaje y desensamblaje de los NPC dependientes del ciclo celular, la organización espacial del complejo Y dentro del andamio del poro y las posibles funciones duales de SEH1 en la envoltura nuclear y los cinetocoros mitóticos. U2OS-CRISPR-SNAPf-SEH1 permite realizar estudios mecánicos de la arquitectura y la dinámica de los poros nucleares en condiciones de expresión fisiológicamente relevantes. |
|---|---|
| Organismo | Humano |
| Tejido | Hueso |
| Enfermedad | Osteosarcoma |
Características
| Edad | 15 años |
|---|---|
| Género | Mujer |
| Etnia | Caucásico |
| Morfología | De tipo epitelial |
| Propiedades de crecimiento | Adherente |
Datos reglamentarios
| Cita | U2OS-CRISPR-SNAPf-SEH1 (número de catálogo de Cytion 300664) |
|---|---|
| Nivel de bioseguridad | 1 |
| NCBI_TaxID | 9606 |
| Depositante | Laboratorio Ellenberg (EMBL) |
| Situación de los OMG | GMO-S1: Esta línea celular de osteosarcoma humano (U2OS-CRISPR-SNAPf-SEH1) contiene una fusión SNAPf-SEH1 mediada por CRISPR que permite el marcaje selectivo de la nucleoporina SEH1. La modificación está presente de forma estable. Esta clasificación sólo se aplica en Alemania y puede diferir en otros países. |
Datos biomoleculares
| Expresión de proteínas | SEH1, SNAPf-tag |
|---|
Manejo de
| Medio de cultivo | McCoys 5a, w: 3,0 g/L Glucosa, w: Glutamina estable, w: 2,0 mM Piruvato sódico, w: 2,2 g/L NaHCO3 (número de artículo de Cytion 820200a) |
|---|---|
| Suplementos | Suplementar el medio con 10% FBS, 3,0 g/L de Glucosa, Glutamina estable, 2,0 mM de Piruvato sódico, 2,2 g/L de NaHCO3, 1% de NEAA |
| Reactivo de disociación | Accutase |
| Subcultivo | Retire el medio antiguo de las células adheridas y lávelas con PBS que carezca de calcio y magnesio. Para matraces T25, utilice 3-5 ml de PBS, y para matraces T75, utilice 5-10 ml. A continuación, cubra completamente las células con Accutase, utilizando 1-2 ml para matraces T25 y 2,5 ml para matraces T75. Deje incubar las células a temperatura ambiente durante 8-10 minutos para desprenderlas. Tras la incubación, mezclar suavemente las células con 10 ml de medio para resuspenderlas y, a continuación, centrifugar a 300xg durante 3 minutos. Desechar el sobrenadante, resuspender las células en medio fresco y transferirlas a nuevos matraces que ya contengan medio fresco. |
| Medio de congelación | Como medio de criopreservación, utilizamos el medio de crecimiento completo (incluido FBS) + 10% DMSO para una viabilidad adecuada tras la descongelación, o CM-1 (número de catálogo 800100 de Cytion), que incluye osmoprotectores optimizados y estabilizadores metabólicos para mejorar la recuperación y reducir el estrés crioinducido. |
| Descongelación y cultivo de células |
|
| Atmósfera de incubación | 37°C, 5%CO2, atmósfera humidificada. |
| Recubrimiento de matraces | Para una fijación y viabilidad óptimas tras la descongelación, recomendamos utilizar matraces o placas recubiertos de colágeno. |
| Procedimiento de congelación | Las líneas celulares crioconservadas se envían en hielo seco en envases validados y aislados con suficiente refrigerante para mantener aproximadamente -78 °C durante el tránsito. A la recepción, inspeccione el envase inmediatamente y transfiera los viales sin demora al almacenamiento adecuado. |
| Condiciones de envío | Las líneas celulares crioconservadas se envían en hielo seco en envases validados y aislados con suficiente refrigerante para mantener aproximadamente -78 °C durante el tránsito. A la recepción, inspeccione el envase inmediatamente y transfiera los viales sin demora al almacenamiento adecuado. |
| Condiciones de almacenamiento | Para la conservación a largo plazo, coloque los viales en nitrógeno líquido en fase vapor a una temperatura aproximada de -150 a -196 °C. El almacenamiento a -80 °C sólo es aceptable como breve paso intermedio antes de la transferencia al nitrógeno líquido. |
Control de calidad / Perfil genético / HLA
| Esterilidad | La contaminación por micoplasma se excluye utilizando tanto ensayos basados en la PCR como métodos de detección de micoplasma basados en la luminiscencia. Para garantizar la ausencia de contaminación bacteriana, fúngica o por levaduras, los cultivos celulares se someten a inspecciones visuales diarias. |
|---|
Acuerdo con terceros
Tenga en cuenta que esta línea celular no está disponible bajo un ATM estándar de Cytion, ya que requiere un acuerdo de terceros y/o está sujeta a negociación con el licenciante original.-
Productos necesarios
Productos necesarios
Medio de congelación CM-1 - 50 mlVariantes de medios de crioconservación: 50 mlEl medio de congelación CM-1 de Cytion es un medio de criopreservación de última generación diseñado para garantizar el máximo nivel de viabilidad y funcionalidad celular tras la descongelación. Este medio versátil es adecuado para un amplio espectro de tipos celulares, incluyendo células humanas y animales, lo que lo convierte en una herramienta esencial para diversas aplicaciones de investigación. Formulado con una combinación meticulosamente equilibrada de crioprotectores y nutrientes esenciales, Freeze Medium CM-1 minimiza la formación de cristales de hielo y el estrés celular durante el proceso de congelación, preservando así la integridad celular.
Las principales características de Freeze Medium CM-1 incluyen:
Amplia compatibilidad: Eficaz para una amplia gama de tipos celulares, incluyendo células primarias, células madre y líneas celulares establecidas.
Alta Viabilidad: Optimizado para maximizar la recuperación y viabilidad celular tras la descongelación, garantizando resultados experimentales fiables.
Listo para usar: Cómodamente preparadas y esterilizadas para su aplicación inmediata, reduciendo el tiempo de preparación y el riesgo de contaminación.
Estabilidad mejorada: Mantiene un rendimiento constante en condiciones de criopreservación estándar, garantizando resultados reproducibles.
Larga vida útil: CM-1 es un medio de criopreservación que contiene suero, listo para usar y que puede almacenarse en el frigorífico hasta un año.
Uso de CM-1 para congelar células
Para utilizar CM-1 para congelar células tanto adherentes como en suspensión, siga estos pasos
Para células adherentes, lavarlas y disociarlas del sustrato de cultivo. Para células en suspensión, proceder directamente al paso siguiente.
Contar las células para asegurarse de que tienen la concentración adecuada.
Centrifugar las células para granularlas y, a continuación, resuspenderlas en medio de congelación CM-1.
Transfiera las células resuspendidas a crioviales.
Utilizar un método de congelación lenta antes de transferir las células al almacenamiento a largo plazo
Método
Descripción
Pasos
❄️
Congelación manual
Un método paso a paso que implica la reducción gradual de la temperatura para garantizar la viabilidad celular
1️⃣ Colocar las células en medio de congelación en un congelador a 4°C durante 40 minutos.
2️⃣ Transferir a un congelador a -80°C durante 24 horas.
3️⃣ Almacenar las células en nitrógeno líquido para su conservación a largo plazo
❄️
Utilización de Mr. Frosty
Un práctico dispositivo que permite velocidades de congelación controladas sin energía eléctrica
1️⃣ Preparar las células en crioviales con medio de congelación.
2️⃣ Colocar los crioviales en el contenedor Mr. Frosty.
3️⃣ Almacenar a -80°C durante 24 horas antes de transferir al nitrógeno líquido
❄️
Congelador de velocidad controlada
Congelador de alta precisión de Thermo Fisher u otros fabricantes diseñado para la reducción controlada de la temperatura
1️⃣ Programar el aparato para que disminuya gradualmente la temperatura.
2️⃣ Colocar las células preparadas en el congelador.
3️⃣ Tras el ciclo de congelación, transfiera las células a nitrógeno líquido
Almacenar los crioviales a temperaturas inferiores a -130°C o en nitrógeno líquido para su conservación a largo plazo.
Ingredientes
Contiene FBS, DMSO, glucosa, sales
Capacidad tampón: pH = 7,2 a 7,6
El Medio de Congelación CM-1 de Cytion ofrece una solución fiable para la criopreservación, asegurando una alta viabilidad celular y funcionalidad post-descongelación para una amplia gama de aplicaciones de investigación.59,00 €*Medio McCoys 5A (modificado), w: 3,0 g/L Glucosa, w: Glutamina estable, w: 2,0 mM Piruvato sódico, w: 2,2 g/L NaHCO3El medio 5A de McCoy es un medio altamente recomendado y especializado, diseñado para facilitar el crecimiento y la replicación de virus en cultivos de células primarias. Ha obtenido un gran reconocimiento por su excepcional rendimiento en diversas aplicaciones de investigación biológica. Una aplicación destacada del medio McCoy's 5A es su utilización en el cultivo de líneas celulares de carcinoma de colon humano. En concreto, se ha empleado en el estudio del receptor acoplado a proteína G que contiene repeticiones ricas en leucina (LGR5) y su papel en la metástasis del cáncer de colon. Este medio se ha empleado con eficacia en el cultivo de varias líneas celulares de carcinoma de colon, entre ellas HCT116, RKO, FET, CBS, HCT116b y TENN, lo que ha permitido a los investigadores profundizar en los mecanismos que subyacen a la metástasis del cáncer de colon. Además de su aplicación en la investigación del cáncer, el medio McCoy's 5A ha demostrado ser indispensable en el estudio de los osteoblastos. Los investigadores que estudian la reactividad iónica de la hidroxiapatita deficiente en calcio en medios de cultivo celular estándar han utilizado este medio para cultivar osteoblastos. Esta aplicación ha facilitado una mejor comprensión de las interacciones entre los osteoblastos y la hidroxiapatita deficiente en calcio, lo que ha contribuido a los avances en el campo de la investigación ósea. El medio McCoy's 5A se formuló meticulosamente modificando los aminoácidos que se encuentran en el medio basal Eagle para proporcionar un soporte óptimo a las células tumorales hepáticas. Esta fórmula enriquecida permite su adecuación a una amplia gama de líneas celulares establecidas, así como a células primarias, lo que mejora aún más su versatilidad y aplicabilidad en diversos entornos de investigación. El medio McCoy's 5A extiende sus efectos bioquímicos y fisiológicos más allá de las células tumorales hepáticas. Se ha empleado con éxito para apoyar el crecimiento en cultivos primarios de médula ósea, piel, encía, riñón, epiplón, suprarrenal, pulmón, bazo, embrión de rata y otros tipos de células. Esta amplia gama de aplicaciones da fe de la gran utilidad del medio McCoy's 5A para apoyar el crecimiento y el mantenimiento de diversos tipos de células para la investigación biológica integral. Formulación Este medio McCoy's 5A (modificado) contiene 3,0 g/l de glucosa, glutamina estable, 2,0 mM de piruvato de sodio y 2,2 g/l de NaHCO3. Control de calidad pH = 7,2 +/
- 0,02 a 20-25 °C. Cada lote ha sido sometido a pruebas de esterilidad y ausencia de micoplasmas y bacterias. Mantenimiento Conservar refrigerado a una temperatura de entre +2 °C y +8 °C en un lugar oscuro. La congelación y el calentamiento a +37 °C minimizan la calidad del producto. No caliente el medio a más de 37 °C ni utilice fuentes de calor incontrolables (por ejemplo, microondas). Si solo se va a utilizar una parte del medio, retire esa cantidad del frasco y caliéntela a temperatura ambiente. La vida útil de cualquier medio, excepto el medio básico, es de 6 a 8 semanas a partir de la fecha de apertura. Composición Componentes mg/L Sales inorgánicasCloruro de calcio x 2H2O132,00 Sulfato de magnesio97,67 Cloruro de potasio400,00 Cloruro de sodio6460,00 Hidrogenofosfato disódico (anhidro)504,00 Otros componentesD(+)-glucosa (anhidra)3000 Glutatión (reducido)0,50 Peptona cárnica600,00 Sal sódica del rojo fenol11 AminoácidosL-alanina13,36 L-arginina x HCl42,14 L-asparagina x H2O45,03 Ácido L-aspártico19,97 L-cisteína x HCl x H2O31,75 L-glutamina (estable)219,15 Ácido L-glutámico22,07 Glicina7,51 L-histidina x HCl x H2O20,96 L-hidroxiprolina19,67 L-isoleucina39,36 L-leucina39,36 L-lisina x HCl36,54 L-metionina14,92 L-fenilalanina16,52 L-prolina17,27 L-serina26,28 L-treonina17,87 L-triptófano3,06 Sal disódica de L-tirosina26,10 L-valina17,57 VitaminasÁcido p-aminobenzoico1,00 Ácido ascórbico0,56 D(+)-biotina0,20 D-Pantotenato cálcico0,20 Cloruro de colina5,00 Ácido fólico10,0 Mioinositol36,00 Nicotinamida0,50 Ácido nicotínico0,50 Piridoxal HCl0,50 Clorhidrato de piridoxina0,50 Riboflavina0,20 Clorhidrato de tiamina0,20 Vitamina B122,0030,00 €*AccutaseVariantes: 100 mlReactivo de disociación celular Accutase
- Una alternativa suave a la tripsina
Accutase es una solución de disociación celular que está revolucionando la industria del cultivo celular. Es una mezcla de enzimas proteolíticas y colagenolíticas que imita la acción de la tripsina y la colagenasa. A diferencia de la tripsina, Accutase no contiene ningún componente mamífero o bacteriano y es mucho más suave con las células, por lo que es una solución ideal para el desprendimiento rutinario de células del material plástico estándar de cultivo de tejidos y del material plástico recubierto de adherencia. En esta entrada del blog, exploraremos los beneficios y usos de Accutase y cómo está cambiando las reglas del juego en el cultivo celular.
Ventajas de Accutase
Accutase tiene varias ventajas sobre las soluciones tradicionales de tripsina. En primer lugar, puede utilizarse siempre que se necesite un desprendimiento suave y eficaz de cualquier línea celular adherente, lo que la convierte en un sustituto directo de la tripsina. En segundo lugar, Accutase funciona extremadamente bien en células madre embrionarias y neuronales, y se ha demostrado que mantiene la viabilidad de estas células después del pasaje. En tercer lugar, Accutase conserva la mayoría de los epítopos para su posterior análisis por citometría de flujo, por lo que es ideal para el análisis de marcadores de superficie celular.
Además, no es necesario neutralizar Accutase al pasar células adherentes. La adición de más medio después de dividir las células diluye Accutase de modo que ya no es capaz de desprender células. Esto elimina la necesidad de un paso de inactivación y ahorra tiempo a los técnicos de cultivo celular. Por último, Accutase no necesita alícuotas y una botella es estable en el frigorífico durante 2 meses.
Aplicaciones de Accutase
Accutase es un sustituto directo de la solución de tripsina y puede utilizarse para el pasaje de líneas celulares. Además, Accutase funciona bien al separar células para el análisis de muchos marcadores de superficie celular mediante citometría de flujo y para la clasificación celular. Otras aplicaciones posteriores del tratamiento con Accutase incluyen el análisis de marcadores de la superficie celular, el ensayo de crecimiento de virus, la proliferación celular, los ensayos de migración de células tumorales, el pasaje celular rutinario, el escalado de la producción (biorreactor) y la citometría de flujo.
Composición de Accutase
Accutase no contiene componentes mamíferos ni bacterianos y es una mezcla enzimática natural con actividad enzimática proteolítica y colagenolítica. Está formulada a una concentración mucho menor que la tripsina y la colagenasa, lo que la hace menos tóxica y más suave, pero igual de eficaz.
Eficacia de Accutase
Accutase ha demostrado ser eficaz en el desprendimiento de células primarias y madre y en el mantenimiento de una alta viabilidad celular en comparación con enzimas de origen animal como la tripsina. el 100% de las células se recuperan al cabo de 10 minutos, y no hay ningún inconveniente en dejar las células en Accutase hasta 45 minutos, gracias a la autodigestión de Accutase.
En resumen
En conclusión, Accutase es una potente solución que está cambiando las reglas del juego en el cultivo celular. Por su naturaleza suave, eficacia y versatilidad, Accutase es la alternativa ideal a la tripsina. Si está buscando una solución fiable y eficaz para el desprendimiento celular, Accutase es la solución para usted.75,00 €*Solución antibiótica/antimicótica (100x)Descripción general del producto
Volumen: 100 ml Almacenamiento: ≤-15°C Esterilidad: Filtrado estéril
La Solución Antibiótica/Antimicótica (100x ) es un concentrado estéril, listo para usar, diseñado para reducir los riesgos de contaminación microbiana en cultivos celulares y aplicaciones de laboratorio relacionadas. Esta solución 100x contiene una combinación bien establecida de penicilina, estreptomicina y anfotericina B, que proporciona una actividad antimicrobiana de amplio espectro contra bacterias Gram-positivas y Gram-negativas, levaduras y hongos filamentosos. La formulación es adecuada para su uso en cultivos de células eucariotas, medios bacterianos y otros sistemas sensibles a la contaminación, lo que favorece unas operaciones de laboratorio limpias y consistentes.
Aplicación y ventajas Optimizada para protocolos de investigación rutinarios, esta solución se utiliza ampliamente para mantener condiciones asépticas en flujos de trabajo de cultivos celulares. Ofrece un rendimiento fiable en entornos sensibles a la contaminación, ayudando a los investigadores a reducir el riesgo de sobrecrecimiento microbiano sin comprometer la salud celular o la reproducibilidad experimental. La formulación filtrada estéril elimina la necesidad de pasos adicionales de solubilización, lo que permite una preparación racionalizada de los medios y reduce la variabilidad en los procedimientos diarios de laboratorio.
Uso y compatibilidad Para alcanzar concentraciones de trabajo estándar, diluya la solución 1:100 en su medio de cultivo completo. El producto es compatible con una amplia gama de líneas celulares de mamíferos y medios basales. Con una disponibilidad de stock constante, los investigadores se benefician de una continuidad de suministro fiable y una planificación logística simplificada. La solución debe almacenarse a ≤ -15 °C y protegerse de ciclos repetidos de congelación-descongelación para mantener la estabilidad. Sólo para uso en investigación. No para uso en procedimientos diagnósticos o terapéuticos. No para uso en humanos o animales.45,00 €*PBSSolución salina tamponada con fosfato (PBS)
La solución salina tamponada con fosfato (PBS) es una solución tampón muy utilizada en la investigación biológica y química. Desempeña un papel crucial en el mantenimiento del equilibrio del pH y la osmolaridad durante diversos procedimientos experimentales, como el procesamiento de tejidos y el cultivo celular. Nuestra solución PBS está meticulosamente formulada con ingredientes de gran pureza para garantizar la estabilidad y fiabilidad en cada experimento. La osmolaridad y las concentraciones de iones de nuestra PBS imitan fielmente las del cuerpo humano, por lo que es isotónica y no tóxica para la mayoría de las células.
Composición de nuestra solución PBS
Nuestra solución PBS es una mezcla de soluciones salinas y tampones de fosfato de grado ultrapuro con pH ajustado. A una concentración de trabajo de 1X, contiene:
8000 mg/L de cloruro sódico (NaCl)
200 mg/L Cloruro potásico (KCl)
1150 mg/L Fosfato sódico dibásico anhidro (Na2HPO4)
200 mg/L Fosfato potásico monobásico anhidro (KH2PO4)
Esta composición garantiza un pH y un equilibrio iónico óptimos, adecuados para una amplia gama de aplicaciones biológicas.
Aplicaciones de nuestra solución PBS
Nuestra solución PBS es ideal para diversas aplicaciones en investigación biológica. Sus propiedades isotónicas y no tóxicas la hacen adecuada para la dilución de sustancias y el enjuague de contenedores celulares. Las soluciones de PBS que contienen EDTA son eficaces para desprender células adheridas y aglomeradas. Sin embargo, los metales divalentes como el zinc no deben añadirse al PBS, ya que pueden provocar precipitación. En tales casos, se recomiendan los tampones de Good. Además, nuestra solución de PBS es una alternativa aceptable al medio de transporte viral para el transporte y almacenamiento de virus de ARN, incluido el SARS-CoV-2.
Control de calidad
Filtrado estéril
Almacenamiento y vida útil
Almacenar a +2°C a +25°C, protegido de la luz.
Una vez abierto, conservar entre 2°C y 25°C y utilizar antes de 24 meses.
Condiciones de envío
Temperatura ambiente
Conservación
Conservar refrigerado a +2°C a +8°C en la oscuridad. Evitar la congelación y el calentamiento frecuente a +37°C, ya que reduce la calidad del producto.
No calentar el medio a más de 37°C ni utilizar fuentes de calor no controladas, como aparatos de microondas.
Si sólo se va a utilizar una parte del medio, retirar la cantidad necesaria y calentarla a temperatura ambiente antes de su uso.
Composición
Categoría
Componentes
Concentración (mg/L)
Sales
Cloruro de potasio
200
Fosfato potásico monobásico anhidro
200
Cloruro sódico
8000
Fosfato sódico dibásico anhidro
115020,00 €* -
Productos relacionados
Productos relacionados
Células U2OS-CRISPR-SNAPf-Nup358/RanBP2Organismo Humano Tejido Hueso Enfermedad Osteosarcoma 800,00 €*